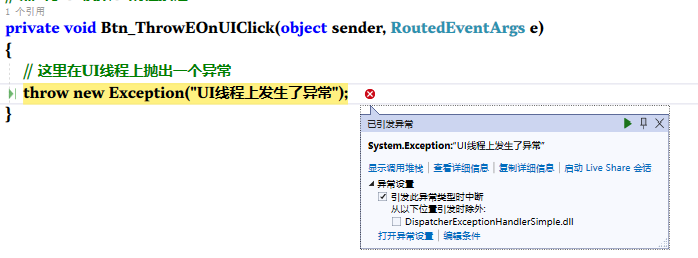
如何捕获代码中出现的所有异常?
解决方案
要捕获所有异常,可以为 Exception 类编写一个异常处理程序,例如:
try:
...
except Exception as e:
...
log('Reason:', e) # Important!除了 SystemExit、KeyboardInterrupt 和 GeneratorExit 之外,上述代码能够捕获所有的异常。如果还想要捕获这三个异常,将 Exception 改为 BaseException 即可。
讨论
有时候,我们很难知道程序会出现的所有可能的异常,这时候捕获所有异常就显得非常重要。当然这也是一种比较省事的做法。
但是当异常真的出现后,我们还是希望知道异常的类型是什么。那么对于异常的实际原因做日志记录或报告就非常必要了。可以考虑下面的一个示例:
def parse_int(s):
try:
n = int(v)
except Exception:
print("Couldn't parse")试着运行上述代码,结果如下:
>>> parse_int('n/a')
Couldn't parse
>>> parse_int('42')
Couldn't parse
>>>此时,你可能会感到非常困惑,为什么函数不能正常工作呢?假如我们把函数修改成以下形式:
def parse_int(s):
try:
n = int(v)
except Exception as e:
print("Couldn't parse")
print('Reason:', e)再次测试,这次错误原因被清楚地指出来了:
>>> parse_int('42')
Couldn't parse
Reason: global name 'v' is not defined
>>>很明显,你应该尽量使用精确的异常类。但是,如果必须捕获所有异常,也应该确保提供高质量的诊断信息,或者将异常抛出去。
参考
《Python Cookbook》第三版
http://python3-cookbook.readthedocs.org/zh_CN/latest/
关于简说基因
生信平台
Galaxy中国(UseGalaxy.cn)致力于打造中国人的云上生物信息基础设施。大量在线工具免费使用。无需安装,用完即走。活跃的用户社区,随时交流使用心得。
生信培训
简说基因的生信培训班,荣获学员的一致好评。如果你也对生物信息学感兴趣,欢迎来跟简说基因,学真生信。
生信分析
我们能够承接所有 NGS 组学数据分析业务,包括但不限于 WGS / WES / RNA-seq 等。基因组组装、注释,以及各种重测序业务都可以与简说基因合作。